設 A 細胞有 2,000 個基因,需繪製 2,000D 的高維度圖,才能完整呈現 A 細胞在空間的定位,顯然這不是我們三維生物可以理解的~
為將相似功能細胞分群在一塊,需要進行降維處理,如同先前曾介紹過菌相 PCA 分析,但基因上下游調控多為複雜非線性關係,且單用 PCA 不適合注重上千顆細胞間相似距離的單細胞,會讓 PCA 圖能解釋的比例甚低。
所以在生資分析時,會先將資料先 PCA 降到 20D,再以 UMAP 與 t-SNE 進行計算~
t-SNE 於 2008 年問世,在適合處理高度非線性資料情況下,能保留局部細胞間的臨近距離,但分析中最常調整參數—困惑度 (Perplexity) 只要一動,會讓全域細胞點間相對距離變化很大,使圖截然不同。
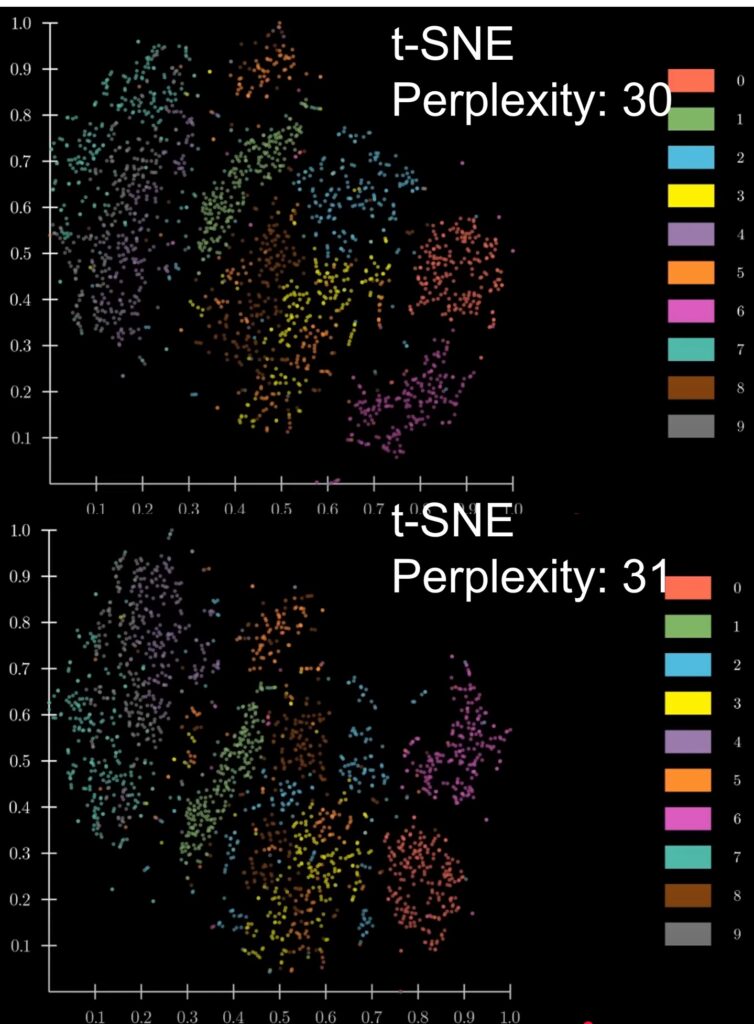
也因此 2018 年 UMAP 被發明,其局部跟全域細胞點的位置更容易維持:藉由調整超參數 (Hyperparameters),下圖中的長毛象甚至可以變成俯視圖,也因此 UMAP 成為近代新寵兒。

結論是兩者藉調整參數是有機會變成教授滿意的結果,但可惜多數人沒有這個 sense QQ
Reference:
YouTube: Latent Space Visualisation: PCA, t-SNE, UMAP | Deep Learning Animated
想看超淺白 PCA 介紹可以看先前發的脆文,本篇同步刊載於 Threads:
PetSci 毛怪實驗紀錄簿 (petsci_note)
