序列剪切 (Trimming) 是門藝術
實務上由於往往無法從文獻、學長姊 (X 中得知,究竟得到的序列是不是含有 Adapter、Barcode,於是嘗試不同的剪切片段就是很重要的步驟。
想像在平行時空下,第七篇 的我們獲得了三張便條紙,上頭寫著每條序列只留下:
1. 0~250 nt 片段 (總長 250 nt,都不切)
qiime dada2 denoise-paired \
--i-demultiplexed-seqs demux.qza \
--p-trim-left-f 0 \
--p-trim-left-r 0 \
--p-trunc-len-f 250 \
--p-trunc-len-r 250 \
--o-table table-dada2-250.qza \
--o-representative-sequences rep-seqs-dada2-250.qza \
--o-denoising-stats stats-dada2-250.qza \
--p-n-threads 82. 10~250 nt 片段 (總長 240 nt)
qiime dada2 denoise-paired \
--i-demultiplexed-seqs demux.qza \
--p-trim-left-f 10 \
--p-trim-left-r 10 \
--p-trunc-len-f 240 \
--p-trunc-len-r 240 \
--o-table table-dada2-240.qza \
--o-representative-sequences rep-seqs-dada2-240.qza \
--o-denoising-stats stats-dada2-240.qza \
--p-n-threads 83. 30~240 nt 片段 (總長 210 nt)
qiime dada2 denoise-paired \
--i-demultiplexed-seqs demux.qza \
--p-trim-left-f 30 \
--p-trim-left-r 30 \
--p-trunc-len-f 210 \
--p-trunc-len-r 210 \
--o-table table-dada2-210.qza \
--o-representative-sequences rep-seqs-dada2-210.qza \
--o-denoising-stats stats-dada2-210.qza \
--p-n-threads 8stats-dada2 資料視覺化
一樣做視覺化輸換 (.qzv),這次只做 stats-dada2.qza。(這邊指令以總長240 nt 為例) 輸入 :
qiime metadata tabulate \
--m-input-file stats-dada-240.qza \
--o-visualization stats-dada2-240.qzv完成後會顯示:
"Saved Visualization to: stats-dada2-240.qzv"stats-dada2 資料解讀
情況一、不合格,Non-Chimeric 通過條數過低 : 0~250 nt 片段
(總長 250 nt,都不切)
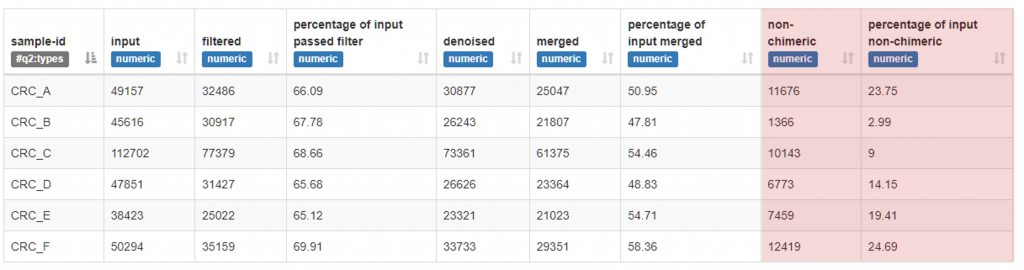
可以發現到如果都沒有切 (或起始切太少),從 merged 到 non-Chimeric 出現驟降(多數剩下不到1%),代表原始序列起始端可能含有 Adapter 或 Barcode,讓 DADA2 誤以為這是 PCR 造成的嵌合體(chimera) (聚合酶表示無辜):
情況二、合格 : 10~250 nt 片段 (總長 240 nt)
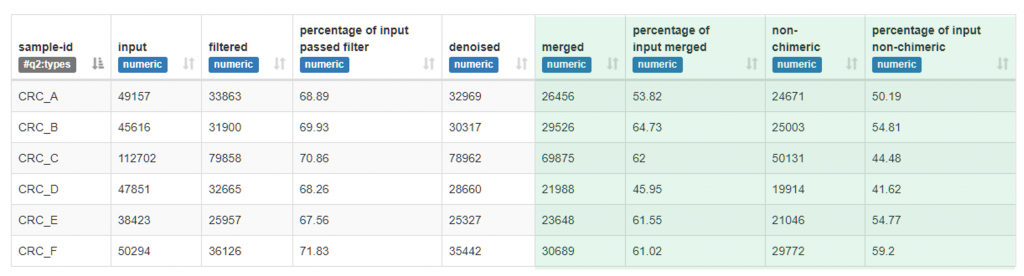
情況三、不合格,Merged 通過條數過低 : 30~240 nt 片段
(總長 210 nt)
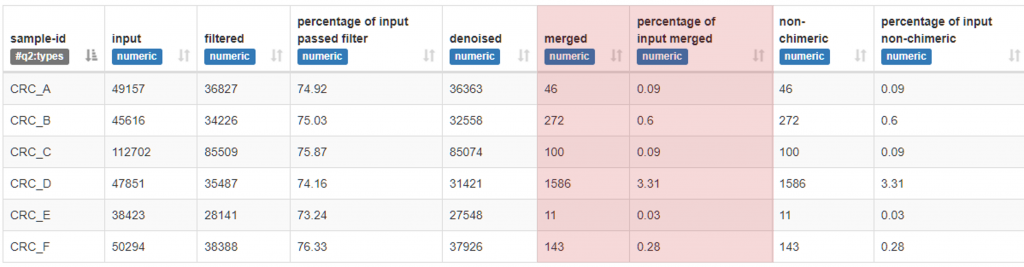
這是剪切過多造成的結果,從 denoised 到 merged 出現驟降(剩下不到 10~30%,甚至 < 1%),代表原始序列起始端與末端剪接過多,雙尾定序 (Paired-end) 的特性就是最後會組裝在一起,詳見 第五篇,若是剪切時切除了兩序列重疊的片段,就會整個樣本的序列都找不到另一半(單身樂園?,最後大家都會被 DADA2 狠心淘汰 (Q
生物資訊的資料分析做實驗相同,都是需要不斷試錯,最後,快快樂樂的拎著 10~250 nt 片段 (總長 240 nt) (即 第八篇 產出的三個.qza 檔案),繼續 QIIME2 分析的旅程~
本篇使用到的輸入/輸出檔案 :
Input: demux.qza
Output: stats-dada2-250.qza、stats-dada2-240.qza、stats-dada2-210.qza、stats-dada2-250.qzv、stats-dada2-240.qzv、stats-dada2-210.qzv
下回是物種分類 (Taxonomy assignment) !