製作一張酷酷的分類柱狀圖 (Taxonomy Bar Plot)
下載訓練好的分類器
如 [第十篇] 所說,先將已訓練好的 Silva 138 V3-V4 分類器 silva138_AB_V3-V4_classifier.qza 放至 Linux 目錄中。Reference : anweshmaile
使用分類器註釋 (Annotation) 序列
使用以下指令,讓分類器註釋我們手上的資料:
qiime feature-classifier classify-sklearn \
--i-classifier silva138_AB_V3-V4_classifier.qza \
--i-reads rep-seqs-dada2-240.qza \
--o-classification taxonomy.qzasklearn 是機器學習廣泛使用的套件,有興趣可以參考 queenawu 大大的 iThome鐵人賽作品。
完成後會顯示:
"Saved FeatureData[Taxonomy] to: taxonomy.qza"輸出的檔案表格化
qiime metadata tabulate \
--m-input-file taxonomy.qza \
--o-visualization taxonomy.qzv完成後會顯示:
"Saved FeatureData[Taxonomy] to: taxonomy.qza"taxonomy.qzv 扔到 QIIME2 VIEW 檢視:
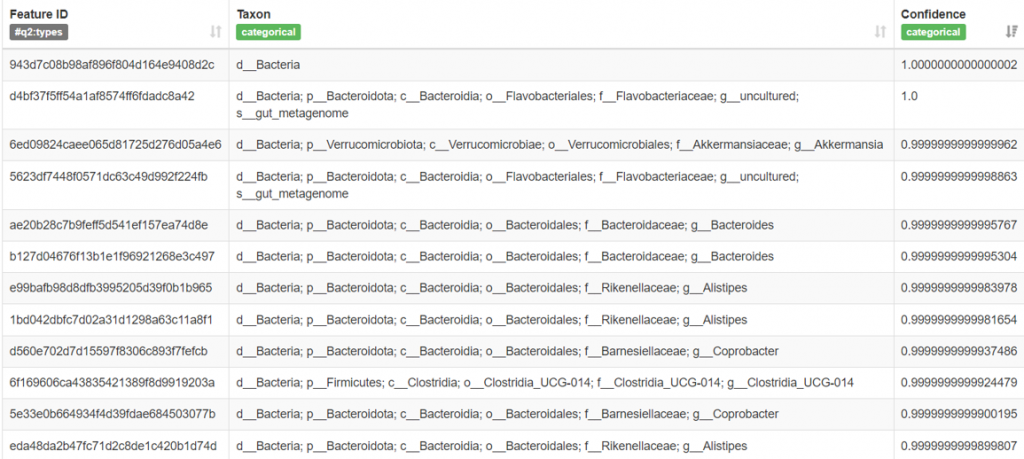
可以在這裡檢視分類器的效果如何,就想像是分類器小朋友繳交的答案卷,Taxon 呈現各階層的結果 (界d 門p 綱c 目o 科f 屬g 種s) ,在Greengene 資料庫則以 D_0, D_1, D_2, D_3 …….數字呈現階層。若是出現許多顯示 Unassigned 或多數無法到 G (Genus) / S (Species),就要考慮分類器是否合適。
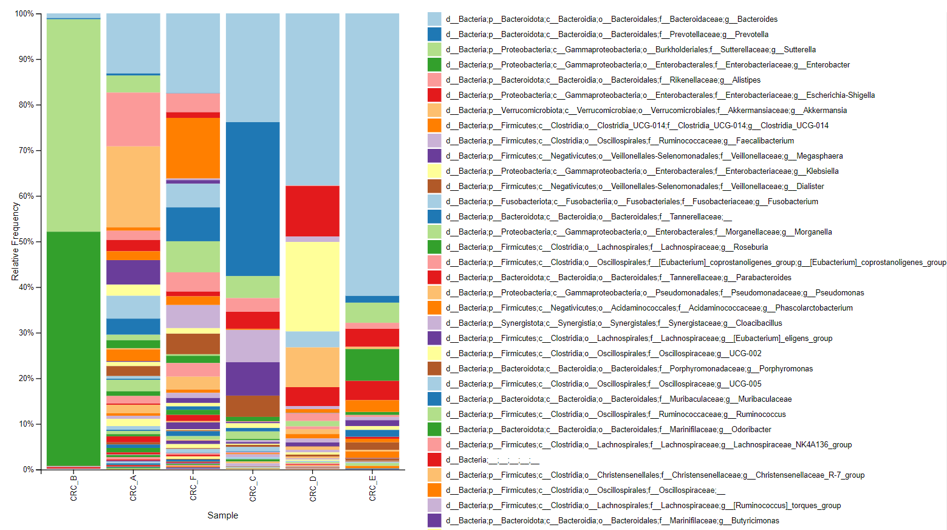
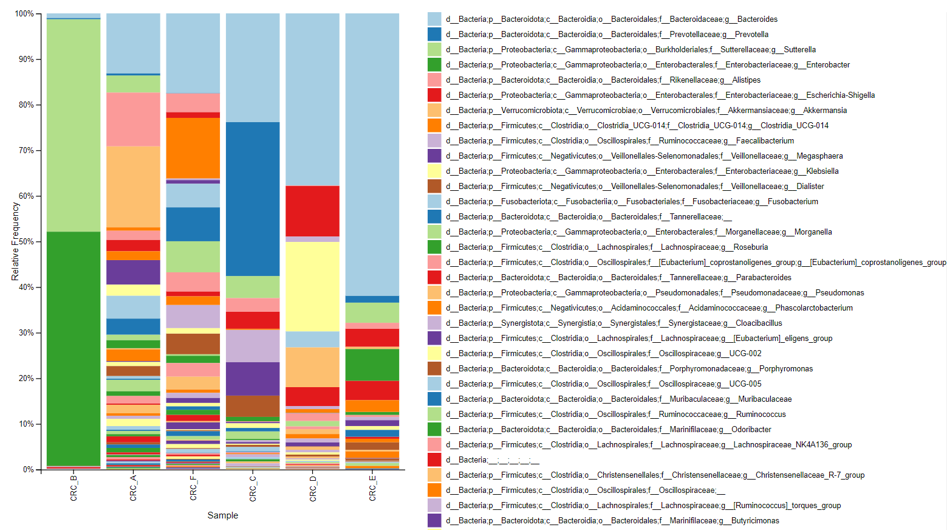
分類柱狀圖製作
仔細觀察開頭的柱狀圖,發現可能需要樣本名稱sample-metadataa.tsv、剛剛的分類結果等資料,如果是照著做下來,這些都之前都已經有了~
qiime taxa barplot \
--i-table table-dada2-240.qza \
--i-taxonomy taxonomy.qza \
--m-metadata-file sample-metadata.tsv \
--o-visualization taxa-bar-plots.qzv完成後會顯示:
"Saved Visualization to: taxa-bar-plots.qzv"taxa-bar-plots.qzv扔到 QIIME2 VIEW 檢視 :
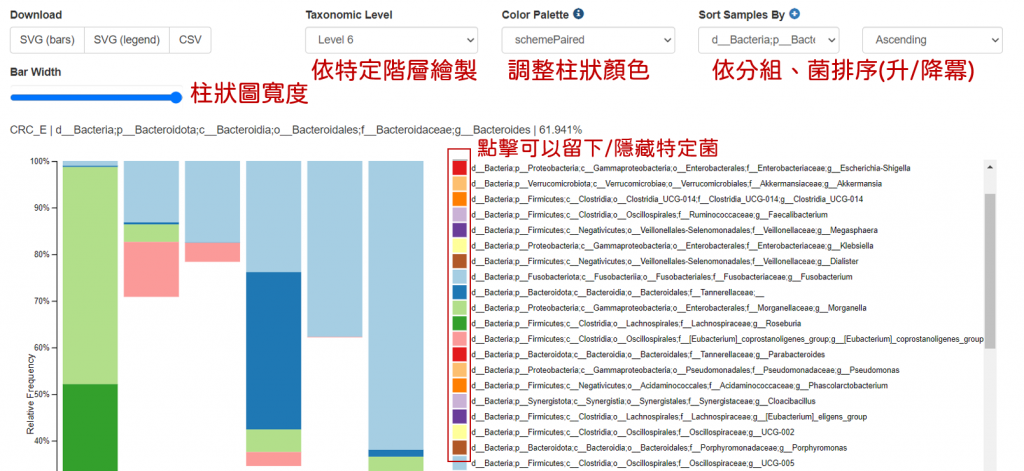
調整好後就會得到一張漂亮的圖啦~
本篇使用到的輸入/輸出檔案 :Input : silva138_AB_V3-V4_classifier.qza、rep-seqs-dada2-240、table-dada2-240.qza、sample-metadata.tsv、taxonomy.qzaOutput: taxonomy.qza、taxonomy.qzv、taxa-bar-plots.qzv
下回繪製 Krona 動態圓餅圖及Top N 分類柱狀圖 !