DADA2 序列品質管制 – 留下好序列,篩掉壞序列
品質管制 (Quality control) 是序列分析重要的一環,為了有系統地留下好序列,DADA2 這個套件包被發明了出來,將 QC 分為修剪 (trimming)、過濾 (filters)、降躁 (denoises)、合併 (merge)、去除重疊 (dereplicates),而 QIIME2 則收錄了 DADA2 讓一切變得更容易。
還記得在 第七篇 中我們獲得了一張便條紙,上頭寫著每條序列都只留下 10~250 nt 片段,因此接下來指令中會需要修剪序列。
然而,每個樣本中都有上萬條序列,裡頭也可能有品質不佳、為了合併而重疊的序列,就需要過濾、降躁、合併、去除重疊,原本的序列們就會像是經過漏斗層層篩選,最後就會剩下好的序列。
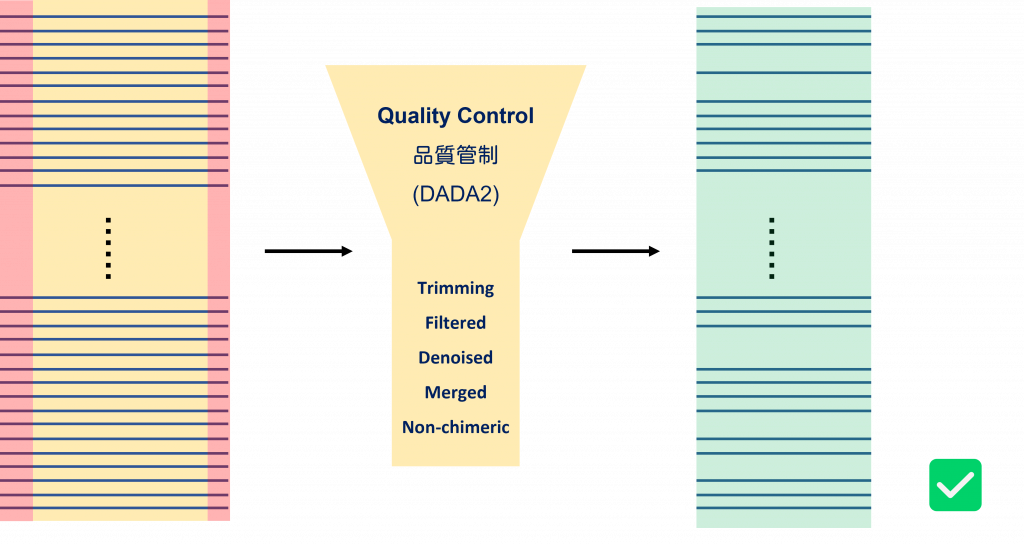
品質管制 (Quality control)
- 記得先啟動 qiime2-2022.8 環境
conda activate qiime2-2022.8
將 第七篇 獲得的 demux.qza 拎來處理處理:
qiime dada2 denoise-paired \
--i-demultiplexed-seqs demux.qza \
--p-trim-left-f 10 \
--p-trim-left-r 10 \
--p-trunc-len-f 240 \
--p-trunc-len-r 240 \
--o-table table-dada2.qza \
--o-representative-sequences rep-seqs-dada2.qza \
--o-denoising-stats stats-dada2.qza \
--p-n-threads 8qiime dada2 denoise-paired: 使用 qiime 軟體 插件為 dada2 的 denoise-paired 函式
–i-demultiplexed-seqs : 輸入的檔案
–p-trim-left-f / –p-trim-left-r: Forward/Reverse 序列起始端切多少,範例是 10 bp
–p-trunc-len-f / –p-trunc-len-r: Forward/Reverse 序列剪切後的總長度,範例末端切 0 bp,所以 240 ~
–o-table: 輸出的檔案
–o-representative-sequences: 輸出的檔案
–o-denoising-stats: 輸出的檔案
–p-n-threads: 要運算的核心數,因設備而異,不清楚可不加這行。調整為 0 就是全力跑╰(°▽°)╯
Reference
完成後會顯示:
'
Saved FeatureTable[Frequency] to: table-dada2.qza
Saved FeatureData[Sequence] to: rep-seqs-dada2.qza
Saved SampleData[DADA2Stats] to: stats-dada2.qza
'輸出的檔案視覺化
輸出產生的檔案除了會做為之後分析的輸入檔案外,也可以做視覺化輸換 (.qzv)。輸入 :
qiime feature-table summarize \
--i-table table-dada2.qza \
--o-visualization table-dada2.qzv \
--m-sample-metadata-file sample-metadata.tsvqiime feature-table tabulate-seqs \
--i-data rep-seqs-dada2.qza \
--o-visualization rep-seqs-dada2.qzvqiime metadata tabulate \
--m-input-file stats-dada2.qza \
--o-visualization stats-dada2.qzv完成後會顯示:
"Saved Visualization to: table-dada2.qzv""Saved Visualization to: rep-seqs-dada2.qzv""Saved Visualization to: stats-dada2.qzv"資料解讀 – 以 stats-dada2 qzv 為例
table-dada2 與 rep-seqs-dada2 兩檔案,會在後續介紹到,我們先來提提常觀察的 stats-dada2:
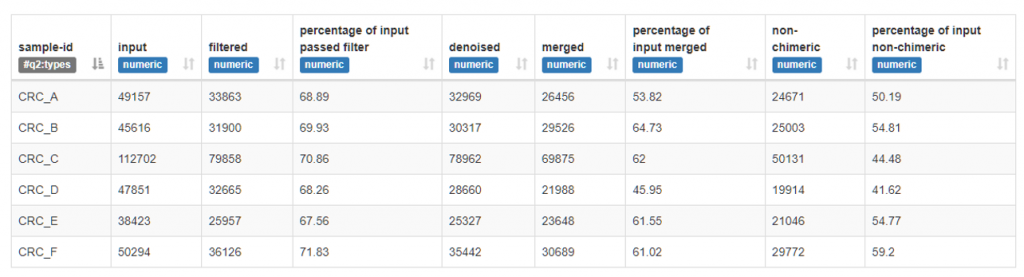
輸入 Input
一開始的尚未進行任何處理的序列總數。
過濾 Filter
目的: 移除有太多低品質(Quality score) mer 出現的序列。
The maxEE parameter sets the maximum number of “expected errors” allowed in a read.
可以想成累加錯誤值,會針對每條序列的每個 mer Quality score 換算為分數進行累加,Quality score 越低,分數則越高,舉例來說 (分數僅示意),若 Quality score 分別為 10, 20, 10, 20, 30…分數則為 0.1 + 0.01 + 0.1 + 0.01 + 0.001 + … + ,整條序列若累積的錯誤分數達到閾值(預設為2),則該條序列就會被拋棄。
降噪 Denoised
目的: 移除 PCR 放大與定序過程中出錯的序列。
像是聚合酶 (Polymerase) 偷懶跳過、引子 (Primer) 亂亂黏,或是溫度條件不穩造成的循環 (Cycle) 未完成即到下一個循環等,都會導致錯誤的序列被製造與放大,會在這個步驟透過演算法篩選。
合併 Merged
目的: 移除 Forward、Reverse 合併時組不起來的序列。
第五篇 中提及雙尾 (pair-end) 是藉由兩段序列組裝成帶有 V3-V4 區的序列,
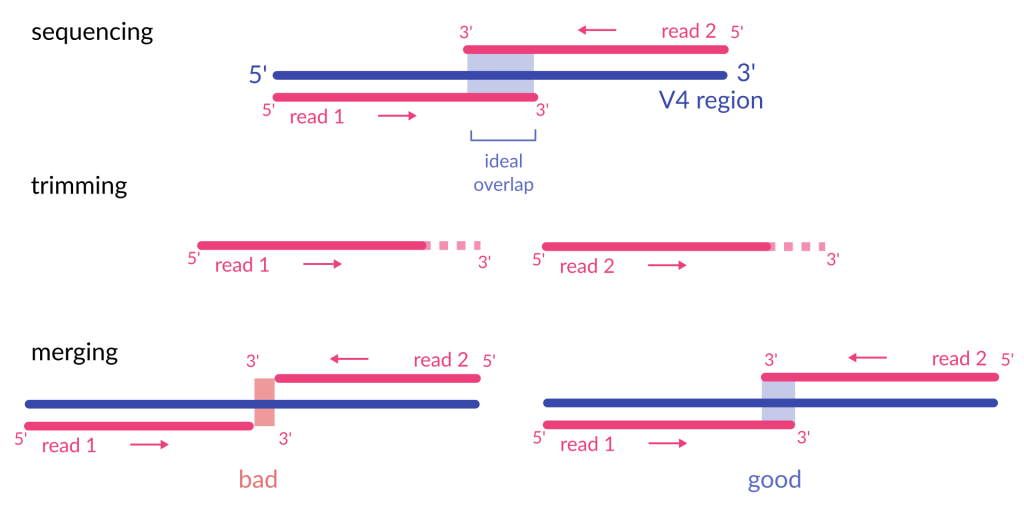
若兩段序列的重疊區域因為各種原因,如品質過低、剪切過多 (如圖示 trimming),都會造成序列合併時找不到另一半,找不到另一半的序列就會被淘汰 (bad) QQ
Reference : ISB Microbiome Course 2020
非嵌合體 Non-Chimeric
目的: 移除因為 PCR 溫度條件出現的嵌合體序列

Reference : ISB Microbiome Course 2020
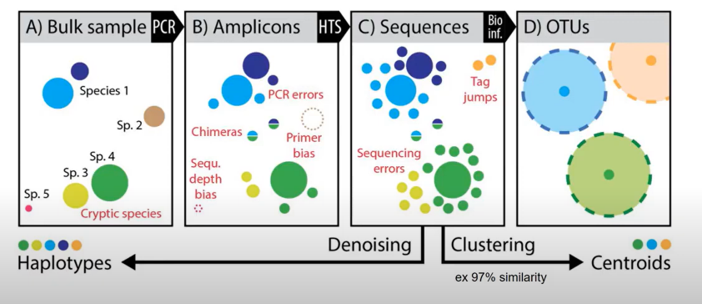
在 PCR 擴增 (Amplicons) 過程中,每一個循環的溫度相當重要,如果可愛的聚合酶在複製的過程中,PCR 機溫度或是其微環境頑皮了,導致聚合酶來不及複製完 (圖示 B),就會出現大大大大大 Primer (圖示 C),並在下一個循環中製造出嵌合體(chimera) (圖示 D)。
經歷層層篩選後的序列,就會成為後續分析的主力,剩下被移除的序列就會消失在這地球上。上述每一步是經由一系列演算法才得以達成,有興趣可以閱讀這篇 Medium,也歡迎拜讀開發者 (Callahan, Benjamin J., et al., 2016),這邊以好讀版為主。
本篇使用到的輸入/輸出檔案 :Input : demux.qzaOutput: table-dada2.qza、rep-seqs-dada2.qza、stats-dada2.qza、table-dada2.qzv、rep-seqs-dada2.qzv、stats-dada2.qzv
下回是常見錯誤篇,從 stats-dada2 看剪切有沒有問題 !