熱圖能一目了然樣本與樣本間的差異
今天天氣晴朗 走輕鬆路線,來畫一張大小朋友教授都愛的熱圖 (Heat map) (? :
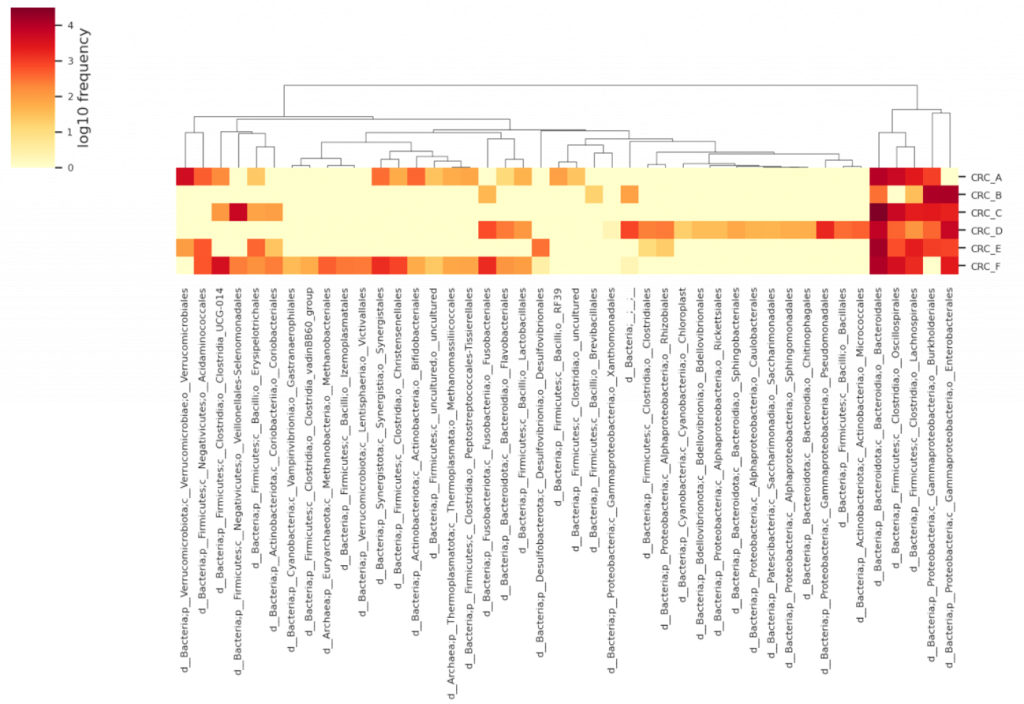
熱圖可以幫助判斷樣本之間的菌種豐富度分布,能夠快速看出哪些是共同菌,哪些是一些樣本才有的菌種。如果在 [第 13篇] 有好好研究親緣關係樹 (Phylogenic tree) 的 iTOL 結果圖,會發現許多特徵ID (Feature ID) 會對應到同一物種,使得在結果圖上同一物種重複出現,但因為在親緣關係樹是以序列比對 (alignment) 角度出發,強調的是序列的相似度(距離),是需要存在的結果。
而在熱圖中,會經歷兩個步驟,先將對應到同一物種的序列進行合併(條數加總),這過程 QIIME2 將其稱為折疊 (collapse),再進行繪製。
Collapse : Collapse groups of features that have the same taxonomic assignment through the specified level. The frequencies of all features will be summed when they are collapsed.
折疊 (Collapse)
進入 qiime2-2022.8 環境後輸入 :
qiime taxa collapse \
--i-table table-dada2-240.qza \
--i-taxonomy taxonomy.qza \
--p-level 4 \
--o-collapsed-table col_table_4.qza–p-level : 這邊就要決定要繪製的分類階層 (taxonomic rank) :
| 參數 | 階層 |
|---|---|
| 1 | 界 Kingdom |
| 2 | 門 Phylum |
| 3 | 綱 Class |
| 4 | 目 Order |
| 5 | 科 Family |
| 6 | 屬 Genus |
| 7 | 種 Species |
–o-collapsed-table : 檔案管理方便,若是有輸出不同階層,記得更改檔名。
完成後會顯示:
qiime feature-table heatmap \
--i-table col_table_4.qza \
--o-visualization heatmap_4.qzv \
--p-color-scheme YlOrRd \
--p-cluster features熱圖 (Heat map) 製作
qiime feature-table heatmap \
--i-table col_table_4.qza \
--o-visualization heatmap_4.qzv \
--p-color-scheme YlOrRd \
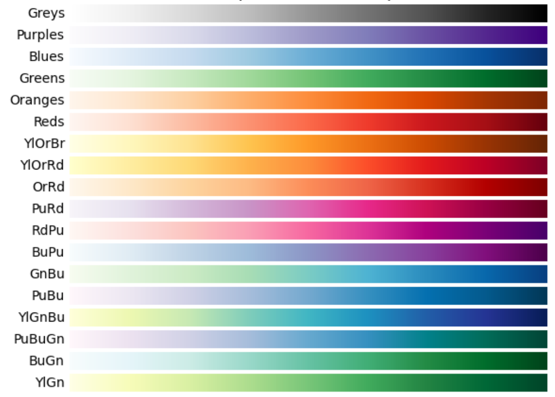
--p-cluster features–p-color-scheme: 好的熱圖顏色帶你上天堂,一般來說會希望越多的顏色越深,還有更多選擇,以下顯示私心推薦的選項,喜歡就直接記住前面的單字於指令中改動 (若此參數不填,跑出來蠻醜的)。
–p-cluster: 可使用 features、samples、both、none,根據序列/樣本/兩者/都不要,進行聚類 (Clustering) 排序,若樣本名稱帶有分組的含意(如 CT_1, CT_2, EXP_3, EXP_4),可以使用 features 就好,就能快速看出實驗組是否與對照組間有菌相差異。
除了上述參數外,還有一些進階選項: 例如 –p-method 依照不同階層式分群法 (hierarchical clustering) 可以分成 : average、centroid、complete、median、single、ward、weighted。預設為 average [選填參數]
完成後會顯示:
'
Saved Visualization to: heatmap_4.qzv
'同樣將 heatmap_4.qzv 拖曳到 QIIME2 VIEW:
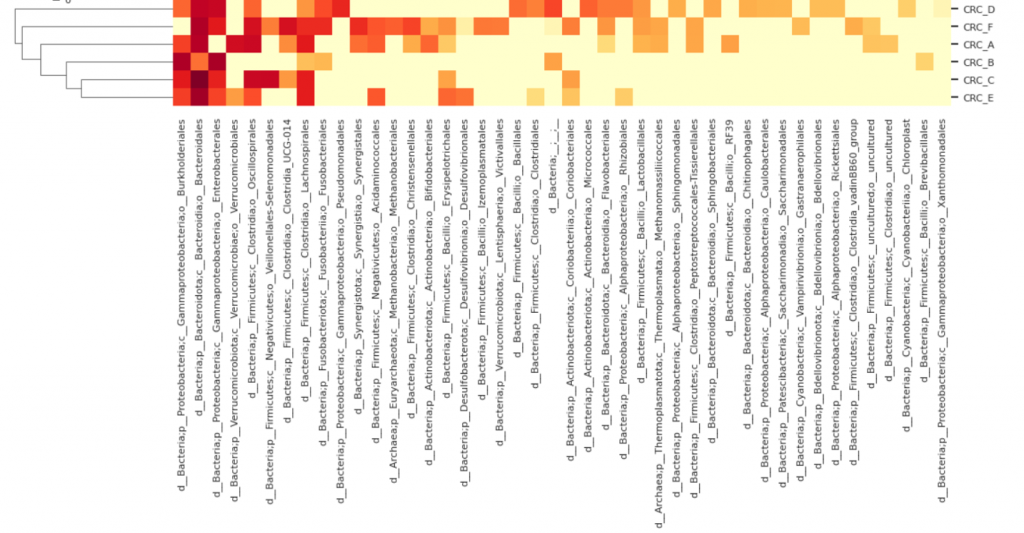
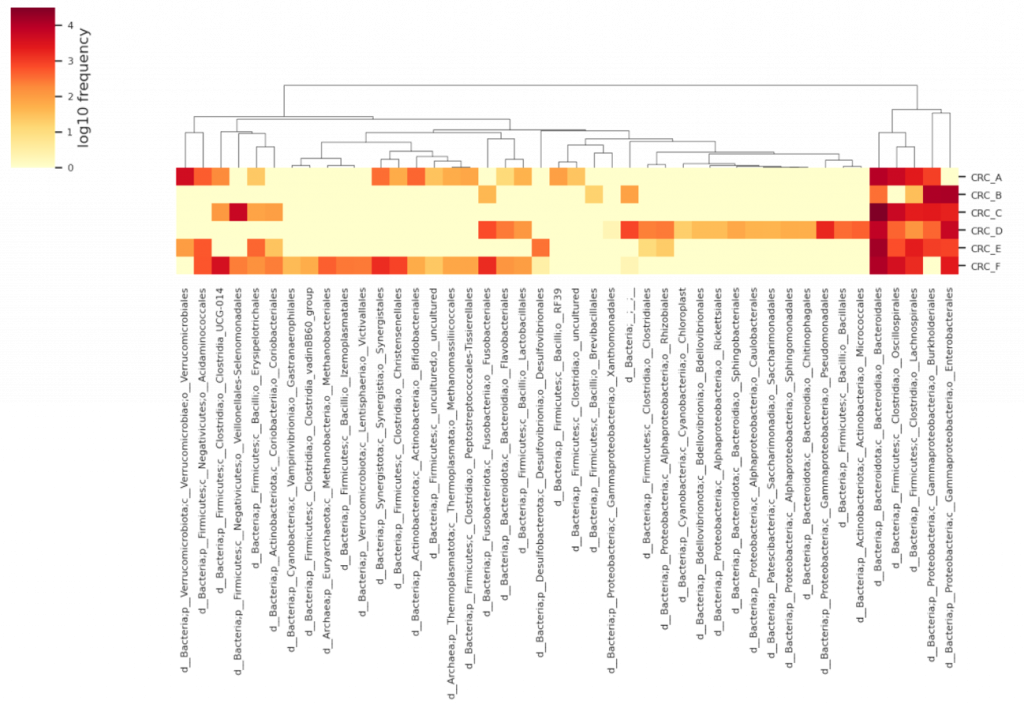
發現差別了嗎? 兩者分別對樣本/特徵ID進行聚類。
本篇使用到的輸入/輸出檔案:Input : table-dada2-240.qza、taxonomy.qza、col_table_4.qzaOutput: col_table_4.qza、heatmap_4.qzv
下回是多樣性統計 !