Alpha Diversity 組內多樣性視覺化呈現方式
Alpha Diversity 強調的是組內的量化數據,接下來就來看看 Alpha Diversity 呈現的兩種常見圖表,稀疏曲線(rarefaction curve)、箱形圖 (Box plot):
稀疏曲線 (rarefaction curve)
檔案: alpha-rarefaction.qzv
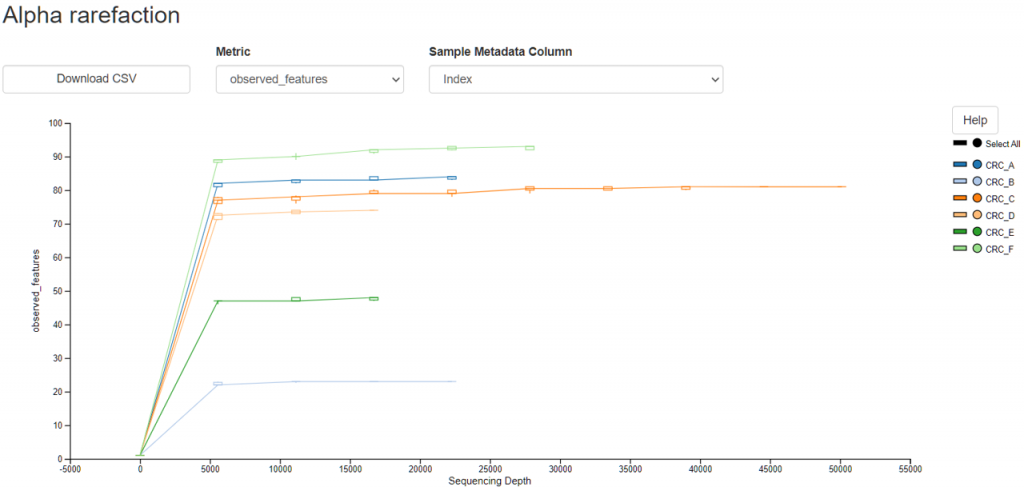
稀疏曲線用於生態學中時,可以確認樣本中的序列數是否足夠代表整個樣本,也可以用來確認這個樣本採樣時是否來自同一批群體 (有無汙染或是來自兩個群體)。延伸閱讀: Whether a group of samples are from the same community。
簡單來說,想像在同一樣本中多次隨機抽樣,每次抽樣的序列數逐漸增加,並觀察每次抽樣所含有的OTU數量,隨著抽樣序列數變多,OTU 數量逐漸飽和,即可以推論樣本中的序列數足夠代表整個樣本。
檔案: alpha-rarefaction.qzv
調整到 Metric : observed_features 及 Index 組:
箱形圖 (Box plot)
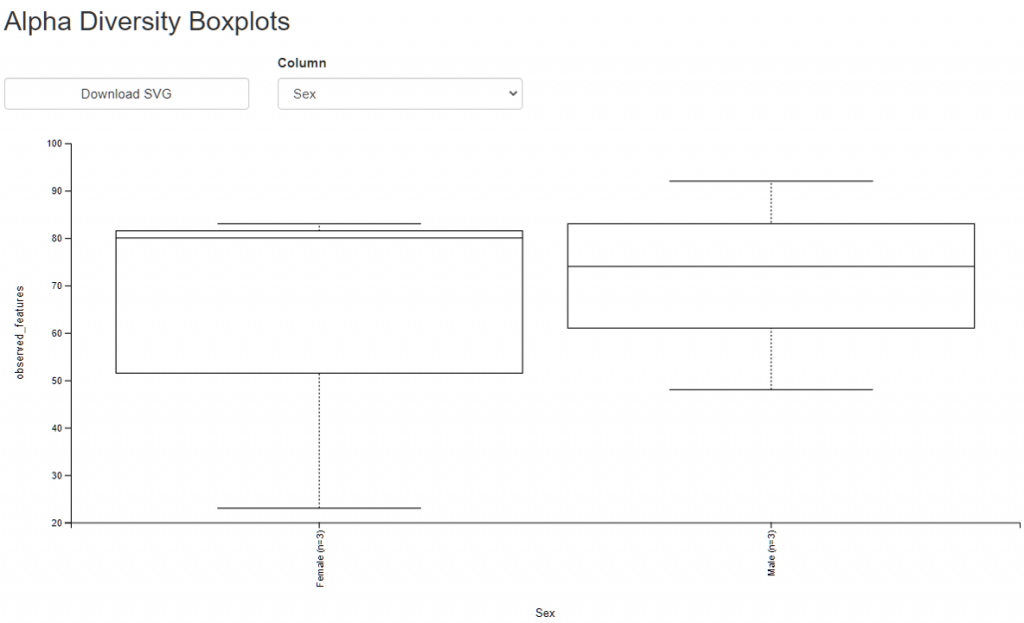
也可以用箱形圖方式呈現樣本多樣性情況,此一方式是可以將各組別放在一起比較,並帶有檢定統計。
資料視覺化輸出 – observed_features_vector
方便與稀疏曲線比較,同樣使用 observed_features
qiime diversity alpha-group-significance \
--i-alpha-diversity core-metrics-results/observed_features_vector.qza \
--m-metadata-file sample-metadata.tsv \
--o-visualization observed_features_vector.qzv放到 QIIME2 VIEW 檢視結果圖
計算多樣性的統計方式
上述的圖表方式其 縱軸 (統計方式) 都是可以替換的,[第 16 篇] 有提到輸出了一坨的檔案,不過有些是明天會說到的 Beta diversity,下面列出各類統計方式供區分與參考 (照字母順序) :
| 檔名 | 方法 |
|---|---|
| bray_curtis_* | Beta diversity |
| evenness_* | Alpha diversity |
| faith_pd_* | Alpha diversity |
| jaccard_* | Beta diversity |
| observed_features_* | Alpha diversity |
| shannon_* | Alpha diversity |
| unweighted_unifrac_* | Beta diversity |
| weighted_unifrac_* | Beta diversity |
雖然看起來很複雜,但其實可以將 Alpha Diversity 統計分為下列三類 :
- 物種豐富度指數 (Species richness) – 物種數量
- observed_features : 組內觀察到的 OTU 數量
- 物種均勻度指數 (Species evenness) – 群集 (community) 中物種數量的分配情況
- evenness
- 物種多樣性指數 (Diversity index) – 綜合豐富度與均勻度的指數
- shannon
- faith_pd (親緣多樣性)
舉例: 物種多樣性指數 faith_pd (Faith Phylogenetic Diversity, PD)
上述指數其實網路上蠻好搜尋到的,我們來看看一個其中一個酷酷的 faith_pd,Faith Phylogenetic Diversity 是根據親緣關係樹 (branch-based) 的物種多樣性指數,如下圖,若兩群集間物種種類相同 (皆為4種)、物種數量的分配相同 (皆各佔25%),無論是豐富度、均勻度,甚至是 shannon 多樣性指數都會相同,但仔細看可以發現,Community A 樹、蝴蝶、花、狐狸彼此親緣差異大,Community B 僅有樹與狐狸的親緣差異較大,因此 Community A 物種間親緣關係差距明顯較 Community B 大:
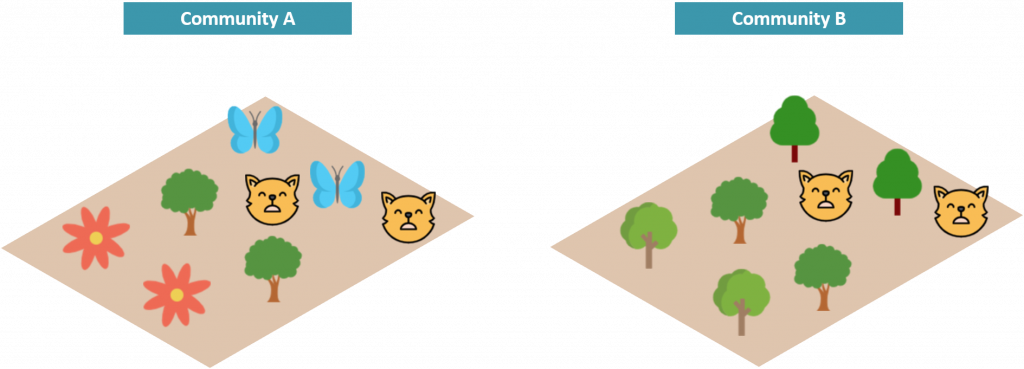
為了能夠呈現這樣子的差異,Faith Phylogenetic Diversity 以關係樹節點的量化方式,示意圖中左圖彼此的親緣關係較遠, 右圖則其中三個物種較為接近:
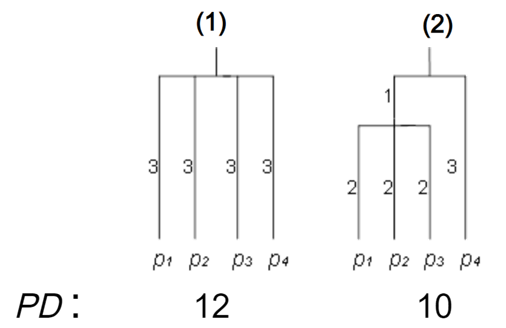
因此,將每個節點數值相加後,PD: A > B,我們將這個概念套用在菌相中,也可以得知組內的菌相親緣關係的情況。
本篇使用到的輸入/輸出檔案:Input : core-metrics-results/observed_features_vector.qza、sample-metadata.tsvOutput: observed_features_vector.qzv、alpha-rarefaction.qzv、core-metrics-results (folder)
下回是 Beta diversity!